核糖核酸定序
此條目需要精通或熟悉生命科學的編者參與及協助編輯。 (2012年2月21日) |
核糖核酸定序,簡稱RNA定序(英語:RNA Sequencing,英文簡稱RNA-Seq,也被稱為全轉錄物組散彈槍法定序 Whole Transcriptome Shotgun Sequencing[1],簡稱WTSS)是基於第二代定序技術的轉錄組學研究方法。RNA定序是使用第二代定序的能力,在給定時刻從一個基因組中,揭示RNA的存在和數量的一個快照的技術。[2]
首先提取生物樣品的全部轉錄的RNA,然後反轉錄為c-DNA後進行的二代高通量定序,在此基礎上進行片段的重疊組裝,從而可得到一個個的轉錄本。進而可以形成對該生物樣品當前發育狀態的基因表現狀況的全局了解(global)。進一步說,若和下一階段的生物樣品的RNA-Seq轉錄組進行比較,則可以得到全部的(在轉錄層面)基因表現的上調及下調--這就形成了表現譜,針對關鍵基因則可以形成你要想要的通路(英語:pathway)的構建。
介紹
[編輯]相較於一個靜態的染色體而言,細胞內的轉錄物組是一個處於不斷變化的動態過程。隨著現在的次世代基因定序(NGS)技術的發展,使得可測得的DNA鹼基覆蓋面增加且樣本輸出的吞吐量增大。有助於對細胞內RNA轉錄物進行定序,提供包括選擇性剪接的轉錄、轉錄後的修飾、基因融合、突變/SNPs以及基因表現量改變等細節[3]。,RNA定序不僅能檢測mRNA的轉錄,還能觀測到包括總RNA和小RNA(miRNA、tRNA和核糖體RNA)在內不同尺度的RNA表現譜[4]。RNA定序還能用來確定外顯子/內含子的邊界,修正之前注釋的5'和3'端基因邊界。未來的RNA定序研究還包括觀察感染時細胞傳導路徑的變化[5]和癌症中不同基因表現程度[6]。下一代基因定序之前,對轉錄物組學和基因表現的研究主要基於基因表現晶片(微陣列),後者包含數以千計用於探測靶向序列的DNA探針,可以得到所有表現出轉錄物的表現譜。基因表現晶片之後,基因表現的系列分析(SAGE)是主要的基因分析技術。 相較於一個靜態的染色體而言,細胞內的轉錄物組是一個處於不斷變化的動態過程。隨著現在的次世代基因定序(NGS)技術的發展,使得可測得的DNA鹼基覆蓋面增加且樣本輸出的吞吐量增大。有助於對細胞內RNA轉錄物進行定序,提供包括選擇性剪接的轉錄、轉錄後的修飾、基因融合、突變/SNPs以及基因表現量改變等細節[7]。,RNA定序不僅能檢測mRNA的轉錄,還能觀測到包括總RNA和小RNA(miRNA、tRNA和核糖體RNA)在內不同尺度的RNA表現譜[8]。RNA定序還能用來確定外顯子/內含子的邊界,修正之前注釋的5'和3'端基因邊界。未來的RNA定序研究還包括觀察感染時細胞傳導路徑的變化[9]和癌症中不同基因表現程度[10]。下一代基因定序之前,對轉錄物組學和基因表現的研究主要基於基因表現晶片(微陣列),後者包含數以千計用於探測靶向序列的DNA探針,可以得到所有表現出轉錄物的表現譜。基因表現晶片之後,基因表現的系列分析(SAGE)是主要的基因分析技術。
相對於RNA定序,基因表現晶片(微陣列)定序結果的覆蓋面很窄,只能覆蓋染色體中1千多萬SNP中的常見等位基因的SNP(50萬到200萬)。因此,現有資料庫中一般沒有罕見等位基因的定序結果,而只有常見的SNP的資料,這對研究者來說是一個重大缺陷。很多癌症源於突變概率小於1%的突變,因而很難被檢測出。但是,基因表現晶片(微陣列)定序在已知的等位基因檢測中仍很重要,使它們非常適合監管機構批准的診斷,如囊性纖維化。
分析
[編輯]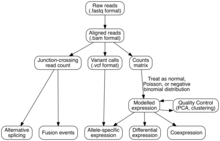
轉錄體組裝
[編輯]有兩種方法用於將原始序列讀數分配給基因體特徵(即組裝轉錄體):
- De novo: 這種方法不需要參考基因體來重建轉錄體,通常基因體未知、不完整或與參考基因體相比有顯著不同時使用[11]。短讀長序列進行de novo組裝時的挑戰包括:(1) 確定哪些序列應連接成連續序列(重疊序列群, contigs)(2) 定序錯誤和其他人為的穩定性 (3) 計算效率。使用在de novo組裝的主要演算法是從重疊圖轉換而來,稱為de Bruijn圖,其將序列讀長切分為長度k的序列並將所有k-mer轉存成雜湊表[12]。使用de Bruijn圖做組裝的工具有 Velvet[13]、Trinity[11]、Oases[14] 和 Bridger[15]。同一樣品的雙端序列和長序列讀長可作為模板或骨架來彌補短讀長序列的缺陷。評估de novo組裝品質的指標包括重疊序列群長度的中位數、重疊序列群數量和 N50[16]。
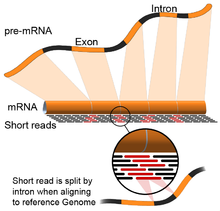
- 引導式組裝:這種方法使用與DNA比對相同的方式,比對序列至參考基因體的非連續部分則需要額外的計算複雜度[17]。這些非連續序列讀數是對剪接產物進行定序的結果(如圖)。通常比對演算法分為兩個步驟:(1) 對齊序列較短的部分 (seed) (2) 使用 動態規劃 來找到最佳比對,有時結合已知的註釋。使用基因體引導比對的工具包括 Bowtie[18] TopHat(基於Bowtie結果對齊剪接點)[19][20]、Subread[21]、STAR[17]、HISAT2[22]、Sailfish[23]、Kallisto[24] 和 GMAP[25]。基因體引導式組裝的品質可以藉由以下兩者來測量:(1) de novo組裝指標(如N50)2)使用精確度、召回率或它們的組合(如F1 score)(與已知的轉錄本、剪接點、基因體和蛋白質序列比較)[16]。此外,可以使用模擬序列讀數的方式進行電腦模擬評估[26][27]。
參考文獻
[編輯]- ^ Ryan D. Morin, Matthew Bainbridge, Anthony Fejes, Martin Hirst, Martin Krzywinski, Trevor J. Pugh, Helen McDonald, Richard Varhol, Steven J.M. Jones, and Marco A. Marra. Profiling the HeLa S3 transcriptome using randomly primed cDNA and massively parallel short-read sequencing. BioTechniques. 2008, 45 (1): 81–94 [2014-02-16]. PMID 18611170. doi:10.2144/000112900. (原始內容存檔於2009-03-21).
- ^ Chu Y, Corey DR. RNA sequencing: platform selection, experimental design, and data interpretation. Nucleic Acid Ther. August 2012, 22 (4): 271–4. PMC 3426205
 . PMID 22830413. doi:10.1089/nat.2012.0367.
. PMID 22830413. doi:10.1089/nat.2012.0367.
- ^ Maher CA, Kumar-Sinha C, Cao X,; et al. Transcriptome sequencing to detect gene fusions in cancer. Nature. March 2009, 458 (7234): 97–101. PMC 2725402
 . PMID 19136943. doi:10.1038/nature07638.
. PMID 19136943. doi:10.1038/nature07638.
- ^ Ingolia NT, Brar GA, Rouskin S, McGeachy AM, Weissman JS. The ribosome profiling strategy for monitoring translation in vivo by deep sequencing of ribosome-protected mRNA fragments. Nat Protoc. August 2012, 7 (8): 1534–50. PMC 3535016
 . PMID 22836135. doi:10.1038/nprot.2012.086.
. PMID 22836135. doi:10.1038/nprot.2012.086.
- ^ Qian F, Chung L, Zheng W; et al. Identification of Genes Critical for Resistance to Infection by West Nile Virus Using RNA-Seq Analysis. Viruses. 2013, 5 (7): 1664–81. PMID 23881275. doi:10.3390/v5071664.
- ^ Beane J, Vick J, Schembri F. Characterizing the impact of smoking and lung cancer on the airway transcriptome using RNA-Seq. Cancer Prev Res (Phila). June 2011, 4 (6): 803–17. PMC 3694393
 . PMID 21636547. doi:10.1158/1940-6207.CAPR-11-0212.
. PMID 21636547. doi:10.1158/1940-6207.CAPR-11-0212.
- ^ Maher CA, Kumar-Sinha C, Cao X,; et al. Transcriptome sequencing to detect gene fusions in cancer. Nature. March 2009, 458 (7234): 97–101. PMC 2725402
 . PMID 19136943. doi:10.1038/nature07638.
. PMID 19136943. doi:10.1038/nature07638.
- ^ Ingolia NT, Brar GA, Rouskin S, McGeachy AM, Weissman JS. The ribosome profiling strategy for monitoring translation in vivo by deep sequencing of ribosome-protected mRNA fragments. Nat Protoc. August 2012, 7 (8): 1534–50. PMC 3535016
 . PMID 22836135. doi:10.1038/nprot.2012.086.
. PMID 22836135. doi:10.1038/nprot.2012.086.
- ^ Qian F, Chung L, Zheng W; et al. Identification of Genes Critical for Resistance to Infection by West Nile Virus Using RNA-Seq Analysis. Viruses. 2013, 5 (7): 1664–81. PMID 23881275. doi:10.3390/v5071664.
- ^ Beane J, Vick J, Schembri F. Characterizing the impact of smoking and lung cancer on the airway transcriptome using RNA-Seq. Cancer Prev Res (Phila). June 2011, 4 (6): 803–17. PMC 3694393
 . PMID 21636547. doi:10.1158/1940-6207.CAPR-11-0212.
. PMID 21636547. doi:10.1158/1940-6207.CAPR-11-0212.
- ^ 11.0 11.1 Grabherr MG, Haas BJ, Yassour M, Levin JZ, Thompson DA, Amit I, Adiconis X, Fan L, Raychowdhury R, Zeng Q, Chen Z, Mauceli E, Hacohen N, Gnirke A, Rhind N, di Palma F, Birren BW, Nusbaum C, Lindblad-Toh K, Friedman N, Regev A. Full-length transcriptome assembly from RNA-Seq data without a reference genome. Nature Biotechnology. May 2011, 29 (7): 644–52. PMC 3571712
 . PMID 21572440. doi:10.1038/nbt.1883.
. PMID 21572440. doi:10.1038/nbt.1883.
- ^ De Novo Assembly Using Illumina Reads (PDF). [22 October 2016]. (原始內容存檔 (PDF)於2020-09-24).
- ^ Zerbino DR, Birney E. Velvet: algorithms for de novo short read assembly using de Bruijn graphs. Genome Research. May 2008, 18 (5): 821–9. PMC 2336801
 . PMID 18349386. doi:10.1101/gr.074492.107.
. PMID 18349386. doi:10.1101/gr.074492.107.
- ^ Oases: a transcriptome assembler for very short reads. [2019-02-16]. (原始內容存檔於2018-11-29).
- ^ Chang Z, Li G, Liu J, Zhang Y, Ashby C, Liu D, Cramer CL, Huang X. Bridger: a new framework for de novo transcriptome assembly using RNA-seq data. Genome Biology. February 2015, 16 (1): 30. PMC 4342890
 . PMID 25723335. doi:10.1186/s13059-015-0596-2.
. PMID 25723335. doi:10.1186/s13059-015-0596-2.
- ^ 16.0 16.1 Li B, Fillmore N, Bai Y, Collins M, Thomson JA, Stewart R, Dewey CN. Evaluation of de novo transcriptome assemblies from RNA-Seq data. Genome Biology. December 2014, 15 (12): 553. PMC 4298084
 . PMID 25608678. doi:10.1186/s13059-014-0553-5.
. PMID 25608678. doi:10.1186/s13059-014-0553-5.
- ^ 17.0 17.1 Dobin A, Davis CA, Schlesinger F, Drenkow J, Zaleski C, Jha S, Batut P, Chaisson M, Gingeras TR. STAR: ultrafast universal RNA-seq aligner. Bioinformatics. January 2013, 29 (1): 15–21. PMC 3530905
 . PMID 23104886. doi:10.1093/bioinformatics/bts635.
. PMID 23104886. doi:10.1093/bioinformatics/bts635.
- ^ Langmead B, Trapnell C, Pop M, Salzberg SL. Ultrafast and memory-efficient alignment of short DNA sequences to the human genome. Genome Biology. 2009, 10 (3): R25. PMC 2690996
 . PMID 19261174. doi:10.1186/gb-2009-10-3-r25.
. PMID 19261174. doi:10.1186/gb-2009-10-3-r25.
- ^ Trapnell C, Pachter L, Salzberg SL. TopHat: discovering splice junctions with RNA-Seq. Bioinformatics. May 2009, 25 (9): 1105–11. PMC 2672628
 . PMID 19289445. doi:10.1093/bioinformatics/btp120.
. PMID 19289445. doi:10.1093/bioinformatics/btp120.
- ^ Trapnell C, Roberts A, Goff L, Pertea G, Kim D, Kelley DR, Pimentel H, Salzberg SL, Rinn JL, Pachter L. Differential gene and transcript expression analysis of RNA-seq experiments with TopHat and Cufflinks. Nature Protocols. March 2012, 7 (3): 562–78. PMC 3334321
 . PMID 22383036. doi:10.1038/nprot.2012.016.
. PMID 22383036. doi:10.1038/nprot.2012.016.
- ^ Liao Y, Smyth GK, Shi W. The Subread aligner: fast, accurate and scalable read mapping by seed-and-vote. Nucleic Acids Research. May 2013, 41 (10): e108. PMC 3664803
 . PMID 23558742. doi:10.1093/nar/gkt214.
. PMID 23558742. doi:10.1093/nar/gkt214.
- ^ Kim, D; Langmead, B; Salzberg, SL. HISAT: a fast spliced aligner with low memory requirements.. Nature Methods. April 2015, 12 (4): 357–60. PMC 4655817
 . PMID 25751142. doi:10.1038/nmeth.3317.
. PMID 25751142. doi:10.1038/nmeth.3317.
- ^ Patro R, Mount SM, Kingsford C. Sailfish enables alignment-free isoform quantification from RNA-seq reads using lightweight algorithms. Nature Biotechnology. May 2014, 32 (5): 462–4. PMC 4077321
 . PMID 24752080. arXiv:1308.3700
. PMID 24752080. arXiv:1308.3700  . doi:10.1038/nbt.2862.
. doi:10.1038/nbt.2862.
- ^ Bray NL, Pimentel H, Melsted P, Pachter L. Near-optimal probabilistic RNA-seq quantification. Nature Biotechnology. May 2016, 34 (5): 525–7. PMID 27043002. doi:10.1038/nbt.3519.
- ^ Wu TD, Watanabe CK. GMAP: a genomic mapping and alignment program for mRNA and EST sequences. Bioinformatics. May 2005, 21 (9): 1859–75. PMID 15728110. doi:10.1093/bioinformatics/bti310.
- ^ Baruzzo G, Hayer KE, Kim EJ, Di Camillo B, FitzGerald GA, Grant GR. Simulation-based comprehensive benchmarking of RNA-seq aligners. Nature Methods. February 2017, 14 (2): 135–139. PMC 5792058
 . PMID 27941783. doi:10.1038/nmeth.4106 (英語).
. PMID 27941783. doi:10.1038/nmeth.4106 (英語).
- ^ Engström PG, Steijger T, Sipos B, Grant GR, Kahles A, Rätsch G, et al. Systematic evaluation of spliced alignment programs for RNA-seq data. Nature Methods. December 2013, 10 (12): 1185–91. PMC 4018468
 . PMID 24185836. doi:10.1038/nmeth.2722 (英語).
. PMID 24185836. doi:10.1038/nmeth.2722 (英語).
外部連結
[編輯]- (英文)RNA-Seq for Everyone (頁面存檔備份,存於網際網路檔案館): a high-level guide to designing and implementing an RNA-Seq experiment.
- (英文)ChIPBase database: 提供的蛋白質編碼基因的表現譜和長鏈非編碼RNA(lncRNAs) (lincRNAs) 從22個組織的RNA定序的資料。
- Martin A. Perdacher (September 2011) Next-Generation Sequencing and its Applications in RNA-Seq[永久失效連結]. Theory part of the Bachelorthesis, Hagenberg. (英文)
